Index >
Results for CNB 71050_0
Input Alignment
CLUSTAL W(1.81) multiple sequence alignment
71050_ENSG00000184260_HUMAN_289_665/1-379 -ACTTGGAGCTGGTGTACTTGGTGACCGCCTTGGTGCCCTCGGACACGGCGTGCTTGGCC
71050_ENSRNOG00000021192_RAT_339_715/1-379 -ACTTGGAGCTGGTGTACTTGGTGACCGCCTTGGTGCCCTCGGACACAGCGTGCTTGGCC
71050_SINFRUG00000141037_FUGU_315_691/1-379 TATTTGGAGCTGGTGTACTTGGTCACGGCCTTGGTGCCCTCGGACACGGCGTGCTTGGCC
71050_ENSDARG00000022900_ZEBRAFISH_292_669/1-379 -ACTTGGAGCTGGTGTATTTGGTCACGGCCTTTGTTCCCTCAGACACTGCGTGTTTGGCC
71050_ENSMUSG00000049529_MOUSE_321_697/1-379 -ACTTGGAGCTGGTGTACTTGGTGACGGCCTTGGTGCCCTCCGACACCGCGTGCTTGGCC
71050_ENSG00000184260_HUMAN_289_665/1-379 AGCTCGCCGGGCAGCAGCAGGCGCACGGCCGTCTGGATCTCGCGGGATGTGATGGTGGAG
71050_ENSRNOG00000021192_RAT_339_715/1-379 AACTCCCCGGGAAGCAACAGACGCACCGCCGTCTGGATCTCCCGGGACGTGATGGTCGAG
71050_SINFRUG00000141037_FUGU_315_691/1-379 AGCTCCCCCGGCAGCAGCAGCCTCACAGCGGTCTGGATCTCCCTGGAGGTGATGGTGGCG
71050_ENSDARG00000022900_ZEBRAFISH_292_669/1-379 AGTTCTCCGGGCAGGAGCAGGCGCACGGCTGTCTGGATCTCCCGGGATGTGATAGTGGAG
71050_ENSMUSG00000049529_MOUSE_321_697/1-379 AGCTCCCCGGGCAGCAGCAGGCGCACGGCCGTCTGGATCTCCCGGGACGTGATGGTCGAG
71050_ENSG00000184260_HUMAN_289_665/1-379 CGCTTGTTGTAGTGCGCCAGGCGGGAAGCCTCTCCCGCGATGCGCTCGAAGATGTCGTTG
71050_ENSRNOG00000021192_RAT_339_715/1-379 CGCTTGTTGTAATGAGCCAGGCGCGACGCCTCGCCCGCGATGCGCTCGAAGATGTCGTTC
71050_SINFRUG00000141037_FUGU_315_691/1-379 CGCTTGTTGTAGTGCGCCAGGCGCGACCCTTCACTGGCGATGCGCTCGAATATGTCGTTC
71050_ENSDARG00000022900_ZEBRAFISH_292_669/1-379 CGCTTGTTGTAATGCGCCAGGCGCGACGCTTCTCCGGCGATGCGCTCGAAGATGTCGTTT
71050_ENSMUSG00000049529_MOUSE_321_697/1-379 CGCTTGTTGTAATGCGCCAGGCGGGACGCCTCGCTCGCGATGCGCTCGAAGATGTCGTTC
71050_ENSG00000184260_HUMAN_289_665/1-379 ACGAAGGAGTTCATGATGCCCATGGCCTTGGACGAGATGCCGGTGTCGGGGTGGACCTGC
71050_ENSRNOG00000021192_RAT_339_715/1-379 ACGAACGAGTTCATTATGCCCATGGCCTTGGAAGAGATGCCCGTGTCCGGATGCACTTGC
71050_SINFRUG00000141037_FUGU_315_691/1-379 ACAAACGAGTTCATGATGCTCATGGCCTTGGAGGAGATGCCCGTGTCTGGGTGCACCTGC
71050_ENSDARG00000022900_ZEBRAFISH_292_669/1-379 ACAAATGAGTTCATAATGCCCATCGCCTTTGAGGAGATGCCAGTGTCCGGGTGGACTTGT
71050_ENSMUSG00000049529_MOUSE_321_697/1-379 ACGAACGAGTTCATGATGCCCATGGCCTTGGAGGAGATACCGGTGTCGGGGTGCACTTGC
71050_ENSG00000184260_HUMAN_289_665/1-379 TTCAGCACCTTGTACACGTAGATGGAGTAGCTCTCTTTGCGGCTGCGCTTGCGCTTCTTG
71050_ENSRNOG00000021192_RAT_339_715/1-379 TTAAGCACCTTGTACACGTACACCGAGTAGCTCTCCTTGCGGCTGCGCTTGCGCTTCTTG
71050_SINFRUG00000141037_FUGU_315_691/1-379 TTCAGCACCTTGTACACGTAAATGGCGTAGCTCTCCTTCCTGTTTTTACGTCGTTTCTTA
71050_ENSDARG00000022900_ZEBRAFISH_292_669/1-379 TTTAGTACTTTGTACACGTAAATGGCGTAACTCTCTTTCCTGGTCTTACGCCTTTTCTTA
71050_ENSMUSG00000049529_MOUSE_321_697/1-379 TTCAGCACCTTGTAGACGTACACCGAGTAGCTCTCCTTGCGGCTGCGCTTGCGCTTCTTG
71050_0.aln
RNAz output
############################ RNAz 0.1 ##############################
Sequences: 5
Columns: 300
Mean pairwise identity: 86.24
Mean single sequence MFE: -129.17
Consensus MFE: -99.54
Energy contribution: -102.30
Covariance contribution: 2.76
Mean z-score: -1.54
Structure conservation index: 0.77
SVM decision value: 0.04
SVM RNA-class probability: 0.555562
Prediction: RNA
######################################################################
>71050_ENSG00000184260_HUMAN_289_665/1-379
ACUUGGAGCUGGUGUACUUGGUGACCGCCUUGGUGCCCUCGGACACGGCGUGCUUGGCCAGCUCGCCGGGCAGCAGCAGGCGCACGGCCGUCUGGAUCUCGCGGGAUGUGAUGGUGGAGCGCUUGUUGUAGUGCGCCAGGCGGGAAGCCUCUCCCGCGAUGCGCUCGAAGAUGUCGUUGACGAAGGAGUUCAUGAUGCCCAUGGCCUUGGACGAGAUGCCGGUGUCGGGGUGGACCUGCUUCAGCACCUUGUACACGUAGAUGGAGUAGCUCUCUUUGCGGCUGCGCUUGCGCUUCUUG
....(((((..((((((..((((...((...(((.(((((.((((((((((.((((.((((...(((((((.(((((((((((.(.((((((.(.((((....)))).))))))).).))))))))))).(.((((...((((((......))))))...)))).)......(((((.(((......))).)))))))))..))).)))).))))))))).))))).))).))))).)).....))))..))))))((((.((.(((.((.......)).))).)).)))))))))... ( -138.60)
>71050_ENSRNOG00000021192_RAT_339_715/1-379
ACUUGGAGCUGGUGUACUUGGUGACCGCCUUGGUGCCCUCGGACACAGCGUGCUUGGCCAACUCCCCGGGAAGCAACAGACGCACCGCCGUCUGGAUCUCCCGGGACGUGAUGGUCGAGCGCUUGUUGUAAUGAGCCAGGCGCGACGCCUCGCCCGCGAUGCGCUCGAAGAUGUCGUUCACGAACGAGUUCAUUAUGCCCAUGGCCUUGGAAGAGAUGCCCGUGUCCGGAUGCACUUGCUUAAGCACCUUGUACACGUACACCGAGUAGCUCUCCUUGCGGCUGCGCUUGCGCUUCUUG
....(((((..((((((..((((...((...(((((..((((((((.((((.(((..((((...(((((((.....((((((......))))))....)))))))..((.((((((((((((..(((((...(.((.(((((...))))).))).))))))))))))).((..(((((....)))))..)).......)))).)).))))..)))))))..))))))))..))))).)).....))))..))))))(((......((((((........))))))...))))))))... ( -127.00)
>71050_SINFRUG00000141037_FUGU_315_691/1-379
UAUUUGGAGCUGGUGUACUUGGUCACGGCCUUGGUGCCCUCGGACACGGCGUGCUUGGCCAGCUCCCCCGGCAGCAGCAGCCUCACAGCGGUCUGGAUCUCCCUGGAGGUGAUGGUGGCGCGCUUGUUGUAGUGCGCCAGGCGCGACCCUUCACUGGCGAUGCGCUCGAAUAUGUCGUUCACAAACGAGUUCAUGAUGCUCAUGGCCUUGGAGGAGAUGCCCGUGUCUGGGUGCACCUGCUUCAGCACCUUGUACACGUAAAUGGCGUAGCUCUCCUUCCUGUUUUUACGUCGUUUCUUA
.....(((((..((((((..((((..(((...(((((.((((((((((((((((((.(((((((((...)).)))....(((((.(((.((.........))))))))))..))))((((((((......)))))))))))))))..((((((..(((.(((.((((((((...(((((....)))))))))..)).)).))).))).))))))......))))))))))).))))).)))...).)))..))))))......(((((((..(........)...))))))))))))... ( -125.80)
>71050_ENSDARG00000022900_ZEBRAFISH_292_669/1-379
ACUUGGAGCUGGUGUAUUUGGUCACGGCCUUUGUUCCCUCAGACACUGCGUGUUUGGCCAGUUCUCCGGGCAGGAGCAGGCGCACGGCUGUCUGGAUCUCCCGGGAUGUGAUAGUGGAGCGCUUGUUGUAAUGCGCCAGGCGCGACGCUUCUCCGGCGAUGCGCUCGAAGAUGUCGUUUACAAAUGAGUUCAUAAUGCCCAUCGCCUUUGAGGAGAUGCCAGUGUCCGGGUGGACUUGUUUUAGUACUUUGUACACGUAAAUGGCGUAACUCUCUUUCCUGGUCUUACGCCUUUUCUUA
....((((...((((((..(((.((.......((((.(((.(((((((((((((((((((...((((.....))))(((((((.(.((((((.(.((((....)))).))))))).).)))))))......)).))))))))))..((.((((((((((((.((.....((..(((((....)))))..)).....)).))))))).....))))).))))))))).))).))))........)))))..))))))......(((((((..((.......))..)))))))..)))).. ( -113.26)
>71050_ENSMUSG00000049529_MOUSE_321_697/1-379
ACUUGGAGCUGGUGUACUUGGUGACGGCCUUGGUGCCCUCCGACACCGCGUGCUUGGCCAGCUCCCCGGGCAGCAGCAGGCGCACGGCCGUCUGGAUCUCCCGGGACGUGAUGGUCGAGCGCUUGUUGUAAUGCGCCAGGCGGGACGCCUCGCUCGCGAUGCGCUCGAAGAUGUCGUUCACGAACGAGUUCAUGAUGCCCAUGGCCUUGGAGGAGAUACCGGUGUCGGGGUGCACUUGCUUCAGCACCUUGUAGACGUACACCGAGUAGCUCUCCUUGCGGCUGCGCUUGCGCUUCUUG
....(((((((((((((.(((((.(((....((...)).))).))))).))))...))))))))).((((.(((.(((((((((..(((((..(((((((((((((((..((..((((((((..(((((...(((..(((((...))))))))..)))))))))))))..))..))))).))..((((..((((.....))))..))))..)))))(((((((((((((((((..........)))))))).......)))))).)))....)))..))))))))))))))))).)))) ( -141.21)
>consensus
_ACUUGGAGCUGGUGUACUUGGUGACGGCCUUGGUGCCCUCGGACACGGCGUGCUUGGCCAGCUCCCCGGGCAGCAGCAGGCGCACGGCCGUCUGGAUCUCCCGGGACGUGAUGGUGGAGCGCUUGUUGUAAUGCGCCAGGCGCGACGCCUCGCCCGCGAUGCGCUCGAAGAUGUCGUUCACGAACGAGUUCAUGAUGCCCAUGGCCUUGGAGGAGAUGCCCGUGUCCGGGUGCACUUGCUUCAGCACCUUGUACACGUAAAUGGAGUAGCUCUCCUUGCGGCUGCGCUUGCGCUUCUUG
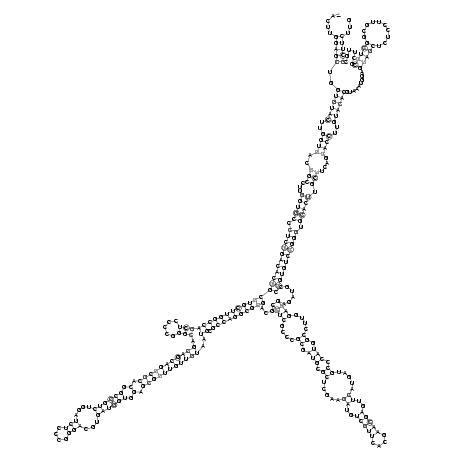
.....(((((..((((((..((((..(((...(((((.((((((((((((((((((((((((((.....))).(((((((((((.(.((((((....(((....)))...)))))).).)))))))))))..)).))))))))))...((((....((.(((.((.....((..(((((....)))))..)).....)).))).))....))))......))))))))))).))))).)))....))))..)))))).........(((((..........)))))......)))))... (-99.54 = -102.30 + 2.76)
71050_0.rnaz
RNAalifold consensus structure
Stefan Washietl
Last modified: Thu Aug 12 14:35:44 CEST 2004