Structure #3208
Summary
| Genome/Assembly | hg17 |
| Chromosome/Contig | chr22 |
| Strand | + |
| Position | 41,335,747 - 41,335,900 |
| Number of sequences | 6 |
| Organisms | human, dog, mouse, rat, chicken, zebrafish, fugu |
| Mean pairwise identity | 80.37 |
| Columns | 165 |
| Mean single MFE | -59.8 |
| Consensus MFE | -46.07 |
| Combinations/base pair | 50 / 38 = 1.32 |
| SCI | 0.77 |
| z-score | -2.46 |
| RNA class probability | 0.944329 |
This structure is part of cluster 65420
Alignment
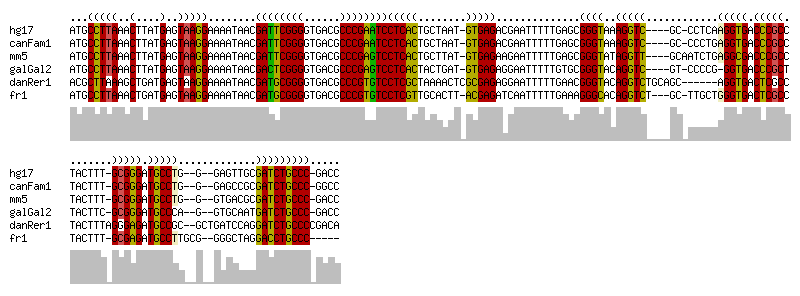
RNAz output
########################### RNAz 0.1.1 ############################# Sequences: 6 Slice: 1 to 165 Columns: 165 Strand: + Mean pairwise identity: 80.37 Mean single sequence MFE: -59.80 Consensus MFE: -46.07 Energy contribution: -43.99 Covariance contribution: -2.07 Mean z-score: -2.46 Structure conservation index: 0.77 SVM decision value: 1.32 SVM RNA-class probability: 0.944329 Prediction: RNA ###################################################################### >hg17.chr22/41335747-41335900 AUGCCUUAAACUUAUGAGUAAGGAAAAUAACGAUUCGGGGUGACGCCCGAAUCCUCACUGCUAAUGUGAGACGAAUUUUUGAGCGGGUAAAGGUCGCCCUCAAGGUGACCCGCCUACUUUGCGGGAUGCCUGGGAGUUGCGAUCUGCCCGACC ...(((((..(....)..)))))........((((((((......))))))))(((((.......))))).............(((((..(((((((.(((.(((((.(((((.......))))).)))))..)))..))))))))))))... ( -60.70) >canFam1.chr10/153-0 AUGCCUUAAACUUAUGAGUAAGGAAAAUAACGAUUCGGGGUGACGCCCGAAUCCUCACUGCUAAUGUGAGACGAAUUUUUGAGCGGGUAAAGGUCGCCCCUGAGGUGACCCGCCUACUUUGCGGGAUGCCUGGGAGCCGCGAUCUGCCCGGCC ..(((.....((((.((((..(.........((((((((......))))))))(((((.......))))).)..)))).)))).((((..((((((((((..(((((.(((((.......))))).))))))))....)))))))))))))). ( -60.70) >mm5.chr15/83507336-83507490 AUGCCUUAAACUUAUGAGUAAGGAAAAUAACGAUUCGGGGUGACGCCCGAGUCCUCACUGCUUAUGUGAGAAGAAUUUUUGAGCGGGUAUAGGUUGCAAUCUGAGGCGACCCGCCUACUUUGCGGGAUGCCUGGGUGACGCGAUCUGCCCGACC ...(((((..(....)..)))))........((((((((......))))))))(((((.......))))).............(((((..(((((((...((.(((((.(((((.......))))).))))).))....))))))))))))... ( -60.60) >galGal2.chr1/142329656-142329504 AUGCCUUAAACUUAUGAGUAAGGAAAAUAACGACUCGGGGUGACGCCCGAGUCCUCACUACUGAUGUGAGAGGAAUUUUUGUGCGGGUACAGGUCGUCCCCGGGUGACCCGCUUACUUCGCGGGAUGCCCAGGUGCAAUGAUCUGCCCGACC ...(((((..(....)..)))))(((((..(((((((((......))))))))(((((.......))))).)..))))).((.((((..(((((((((((.(((((.(((((.......))))).))))).)).)..)))))))))))))). ( -61.70) >danRer1.chrNA/108870137-108870294 ACGCUUAAAGCUGAUGAGUAAGGAAAAUAACGAUGCGGGGUGACGCCCGUGUCCUCGCUAAAACUCGCGAGAGGAAUUUUUGAACGGGUACAGGUCUGCAGCAGGUGACUCGCCUACUUUAGGGAGAUGCCGCGCUGAUCCAGGAUCUGCCCCGACA ..(((((.......)))))...((((((..(((((((((......))))))))(((((........))))).)..))))))...((((..(((((((.((((.((((.(((.((((...))))))).))))..)))).....))))))).))))... ( -57.40) >fr1.chrUn/78555361-78555513 AUGCCUUAAACUGAUGAGUAAGGAAAAUAACGAUGCGGGGUGACGCCCGUGUCCUCGUUGCACUUACGAGAUCAAUUUUUGAAAGGGCACAGGUCUGCUUGCUGGGUGACUCGCCUACUUUGCGAGAUGCCUUGCGGGGCUAGGACCUGCCC .(((((((((.((((..(((((...((..(.((((((((......)))))))).)..))...)))))...)))).))).....))))))(((((((.(((((.(((((.(((((.......))))).))))).)))))....)))))))... ( -57.70) >consensus AUGCCUUAAACUUAUGAGUAAGGAAAAUAACGAUUCGGGGUGACGCCCGAGUCCUCACUGCUAAU_GUGAGACGAAUUUUUGAGCGGGUACAGGUC____GC_CCCCGAGGUGACCCGCCUACUUU_GCGGGAUGCCUG__G__GAGCCACGAUCUGCCC_GACC ...(((((..(....)..)))))........((((((((......))))))))(((((........)))))..............((((..(((((............(((((.(((((........))))).))))).............)))))))))..... (-46.07 = -43.99 + -2.07)
Consensus structure
Secondary structure graph

Montain plot
Dotplot